peptides
spectra
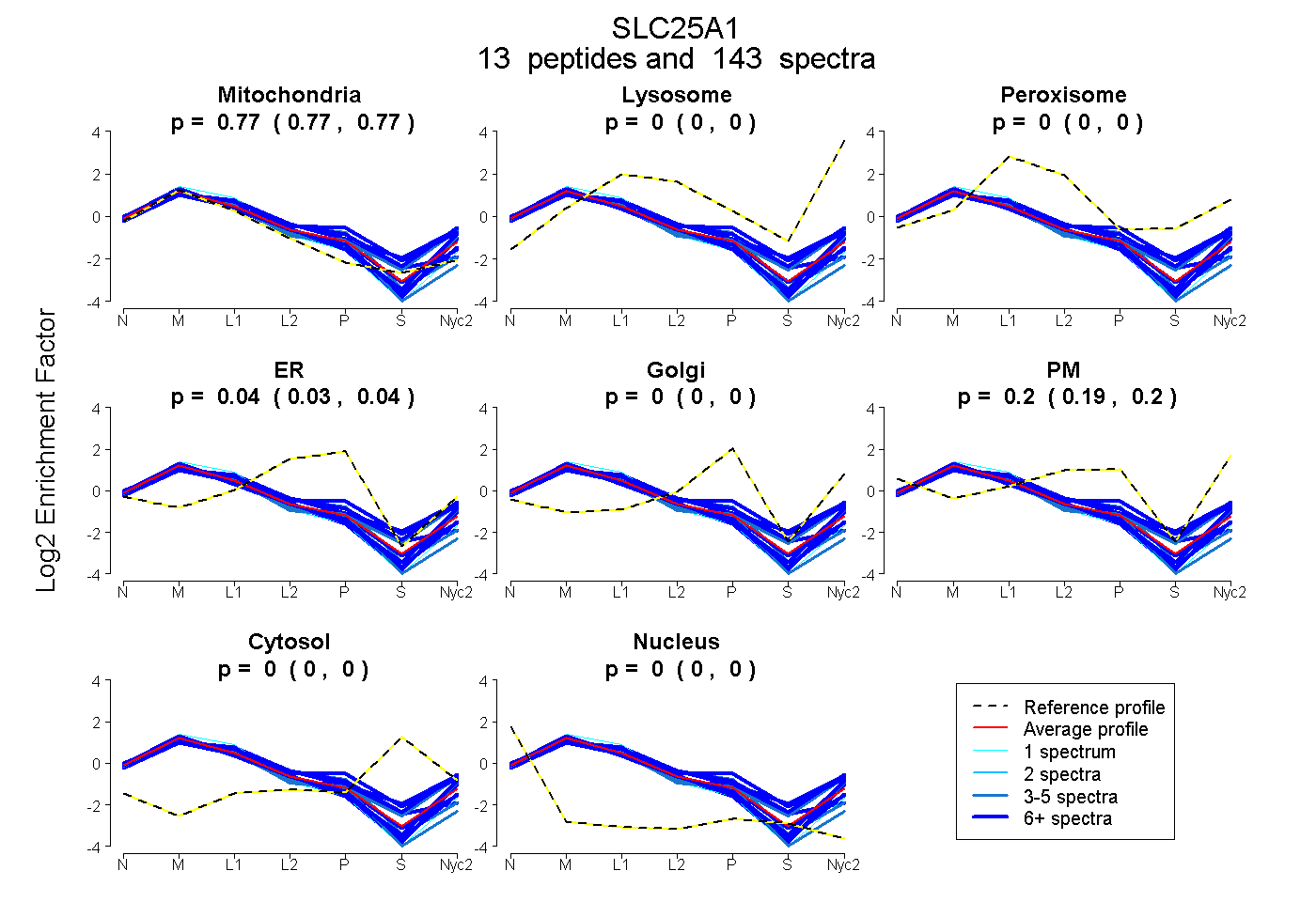
0.766 | 0.771
0.000 | 0.000
0.000 | 0.000
0.027 | 0.042
0.000 | 0.000
0.186 | 0.204
0.000 | 0.000
0.000 | 0.000
peptides
spectra
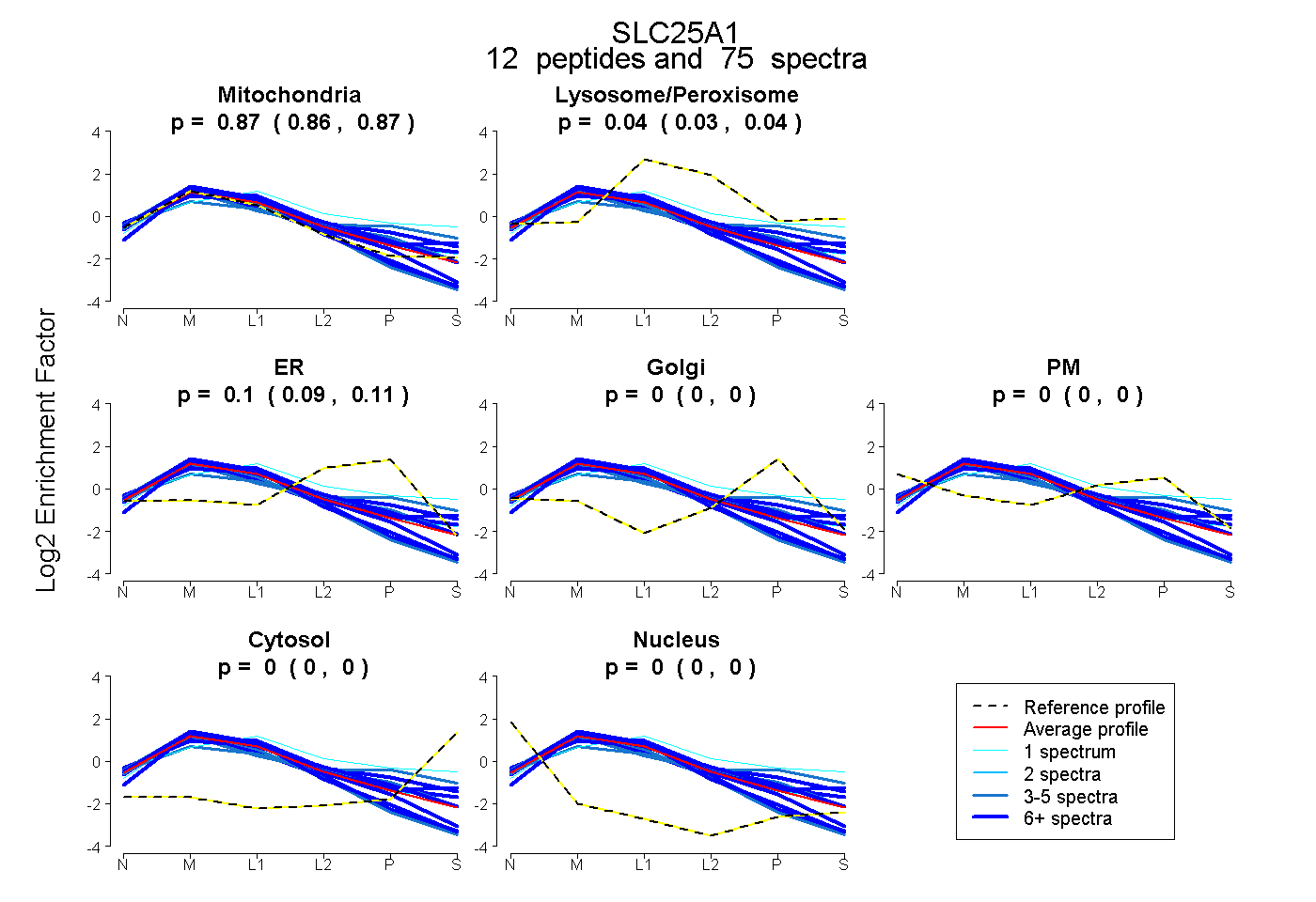
0.857 | 0.873
0.027 | 0.044
0.088 | 0.107
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
143 spectra |
 |
0.769 0.766 | 0.771 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.035 0.027 | 0.042 |
0.000 0.000 | 0.000 |
0.196 0.186 | 0.204 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
75 spectra |
 |
0.866 0.857 | 0.873 |
0.036 0.027 | 0.044 |
0.098 0.088 | 0.107 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
0.000 0.000 | 0.000 |
| 6 spectra, TQLQLDER | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 15 spectra, GFFHGVR | 0.939 | 0.000 | 0.061 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 6 spectra, SHGVLGLYR | 0.810 | 0.055 | 0.135 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, MQGLEAHK | 0.785 | 0.000 | 0.215 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 1 spectrum, LTHPGK | 0.353 | 0.473 | 0.000 | 0.132 | 0.000 | 0.042 | 0.000 | |||
| 6 spectra, GIGDCVR | 0.784 | 0.176 | 0.003 | 0.000 | 0.037 | 0.000 | 0.000 | |||
| 1 spectrum, FGMFEFLSNHMR | 0.879 | 0.047 | 0.074 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 4 spectra, GTYQGLTATVLK | 0.473 | 0.243 | 0.000 | 0.244 | 0.000 | 0.040 | 0.000 | |||
| 6 spectra, FIHDQTSSNPK | 0.639 | 0.228 | 0.000 | 0.133 | 0.000 | 0.000 | 0.000 | |||
| 8 spectra, NTLDCGVQILK | 0.727 | 0.174 | 0.000 | 0.000 | 0.053 | 0.046 | 0.000 | |||
| 13 spectra, FFVMTSLR | 1.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | |||
| 5 spectra, QGSNQAIR | 0.987 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.013 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
435 spectra |
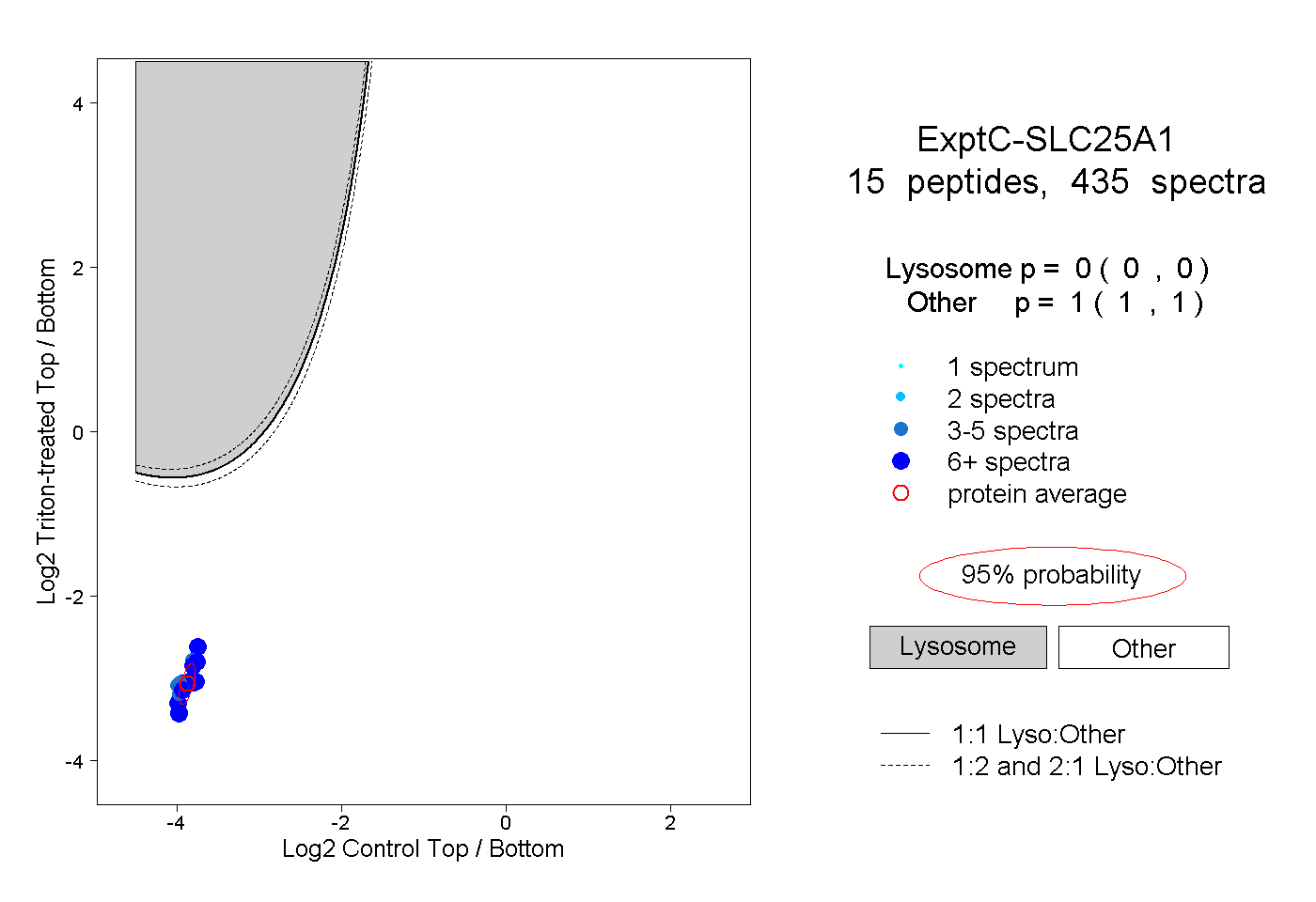 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
41 spectra |
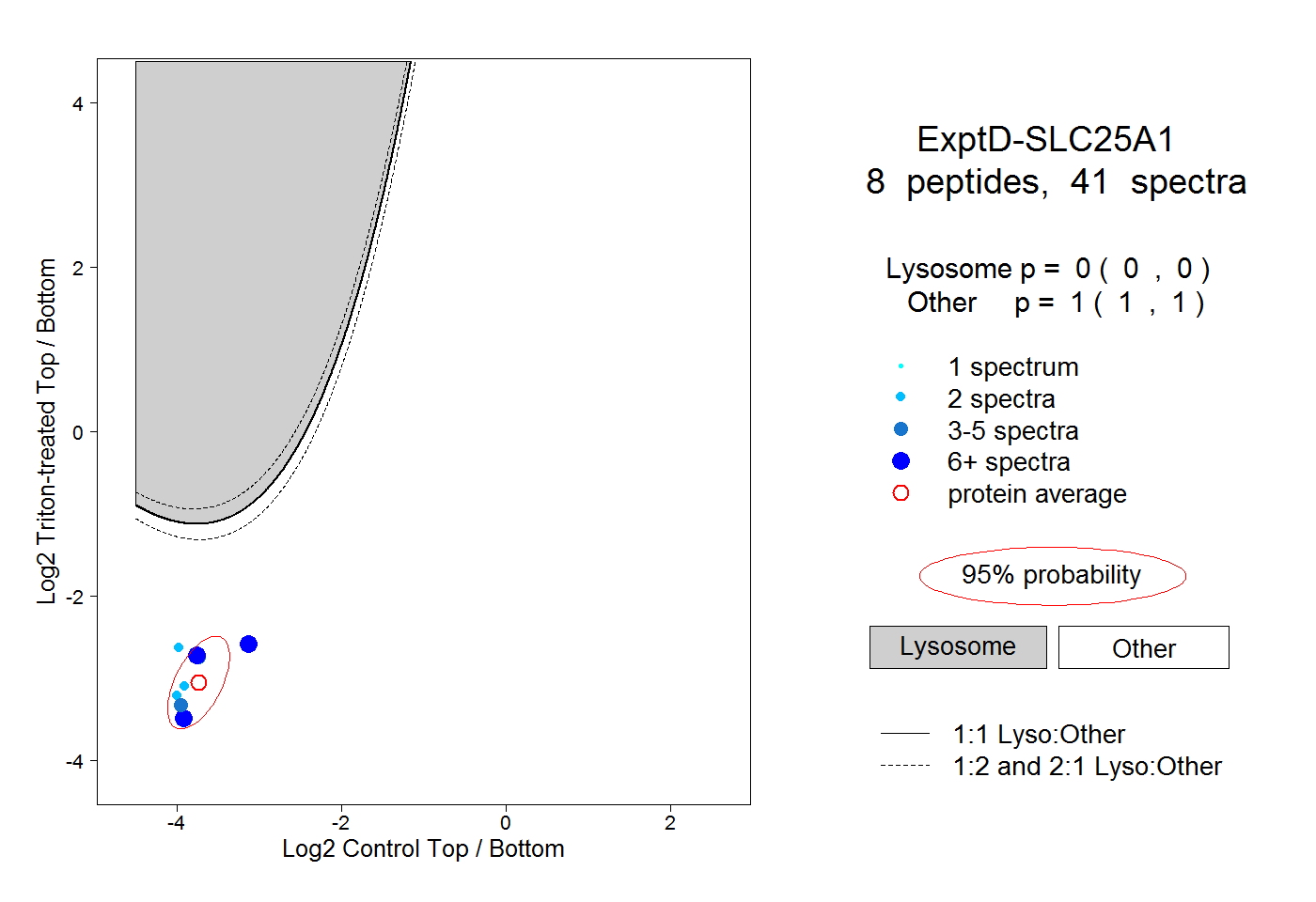 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |