peptides
spectra
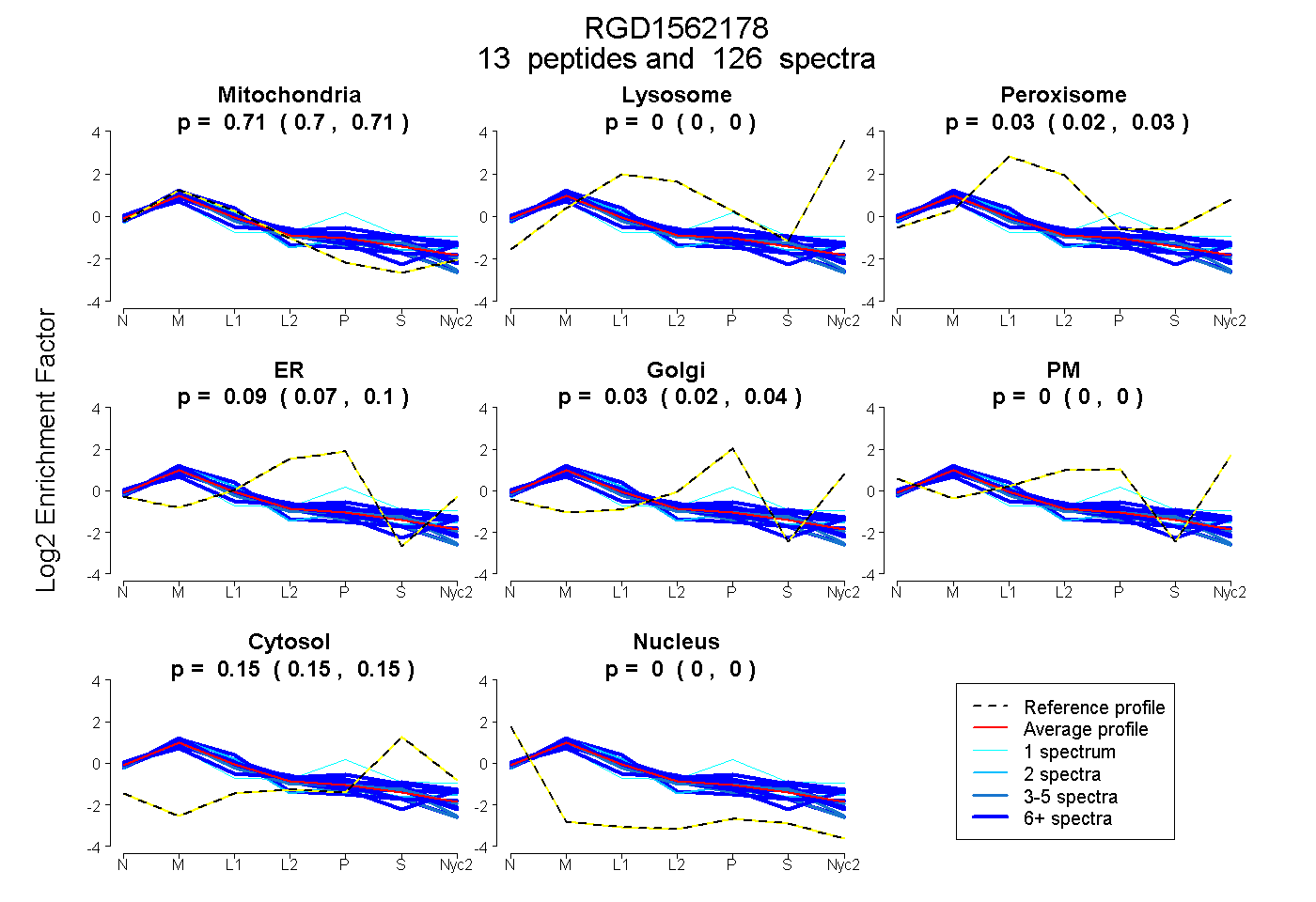
0.705 | 0.711
0.000 | 0.000
0.021 | 0.030
0.073 | 0.096
0.019 | 0.041
0.000 | 0.000
0.146 | 0.152
0.000 | 0.000
peptides
spectra
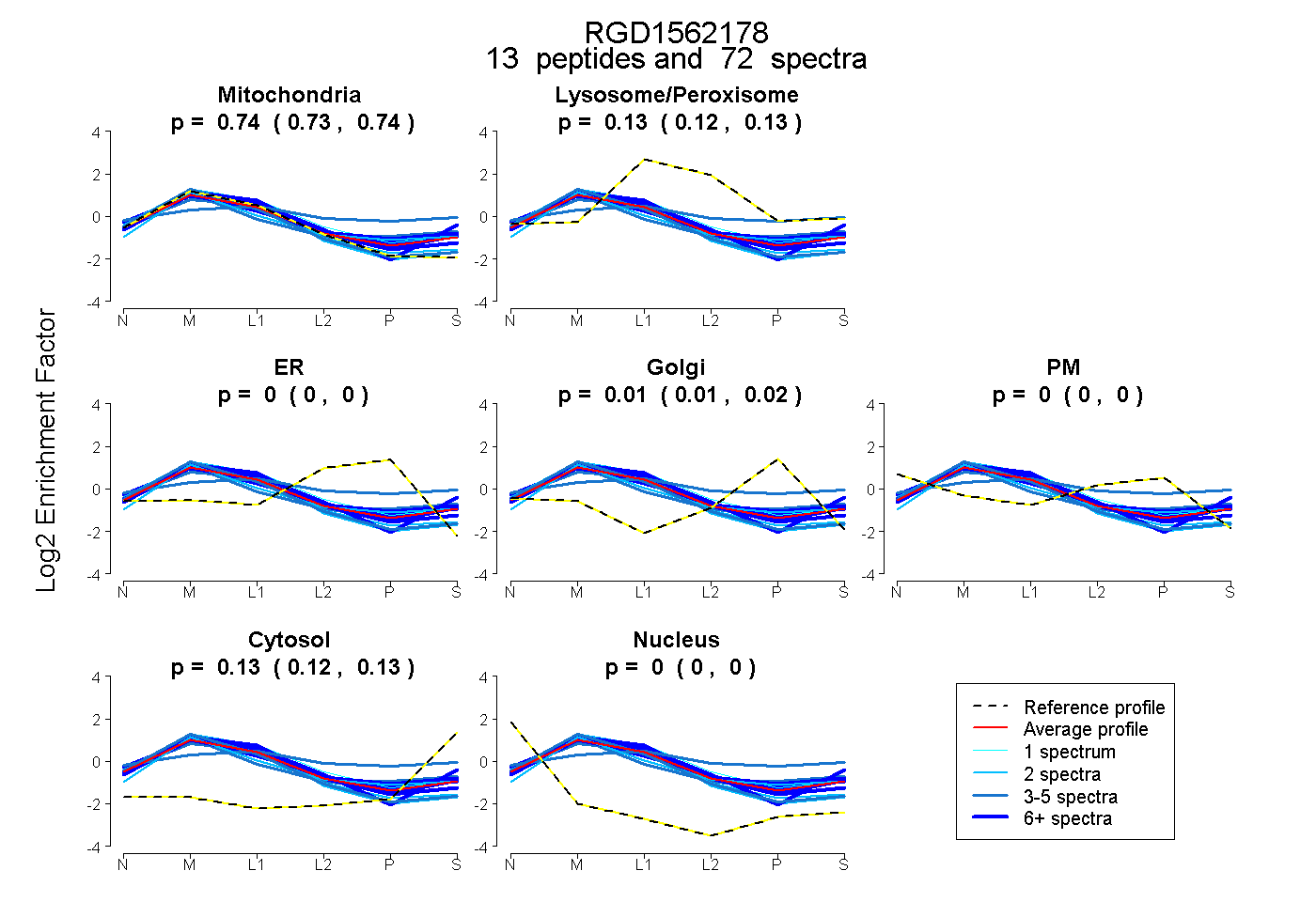
0.727 | 0.742
0.121 | 0.129
0.000 | 0.000
0.006 | 0.020
0.000 | 0.000
0.121 | 0.131
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
126 spectra |
 |
0.708 0.705 | 0.711 |
0.000 0.000 | 0.000 |
0.026 0.021 | 0.030 |
0.086 0.073 | 0.096 |
0.031 0.019 | 0.041 |
0.000 0.000 | 0.000 |
0.149 0.146 | 0.152 |
0.000 0.000 | 0.000 |
||
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
72 spectra |
 |
0.735 0.727 | 0.742 |
0.125 0.121 | 0.129 |
0.000 0.000 | 0.000 |
0.013 0.006 | 0.020 |
0.000 0.000 | 0.000 |
0.126 0.121 | 0.131 |
0.000 0.000 | 0.000 |
| 4 spectra, AVLLGPPGAGK | 0.604 | 0.180 | 0.000 | 0.076 | 0.000 | 0.141 | 0.000 | |||
| 3 spectra, NLETPSCK | 0.186 | 0.397 | 0.000 | 0.096 | 0.137 | 0.184 | 0.000 | |||
| 11 spectra, LAENFCVCHLATGDMLR | 0.662 | 0.163 | 0.000 | 0.000 | 0.000 | 0.175 | 0.000 | |||
| 2 spectra, GTQAPK | 0.987 | 0.000 | 0.000 | 0.000 | 0.000 | 0.009 | 0.004 | |||
| 2 spectra, QAEMLDDLMDK | 0.683 | 0.082 | 0.000 | 0.090 | 0.000 | 0.145 | 0.000 | |||
| 14 spectra, LVSDEMVVELIEK | 0.644 | 0.158 | 0.000 | 0.069 | 0.000 | 0.129 | 0.000 | |||
| 8 spectra, NGFLLDGFPR | 0.824 | 0.113 | 0.000 | 0.000 | 0.000 | 0.062 | 0.000 | |||
| 1 spectrum, ATMDAGK | 0.694 | 0.216 | 0.000 | 0.013 | 0.000 | 0.077 | 0.000 | |||
| 4 spectra, SDDNEK | 0.947 | 0.000 | 0.000 | 0.000 | 0.000 | 0.044 | 0.009 | |||
| 3 spectra, AMVASGSELGK | 0.727 | 0.038 | 0.000 | 0.068 | 0.000 | 0.167 | 0.000 | |||
| 12 spectra, LEAYHTQTTPLVEYYR | 0.728 | 0.112 | 0.000 | 0.000 | 0.011 | 0.149 | 0.000 | |||
| 2 spectra, DDITGEPLIR | 0.941 | 0.004 | 0.000 | 0.000 | 0.000 | 0.054 | 0.000 | |||
| 6 spectra, APNALAPEPEHPK | 0.697 | 0.115 | 0.000 | 0.000 | 0.070 | 0.118 | 0.000 |
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
602 spectra |
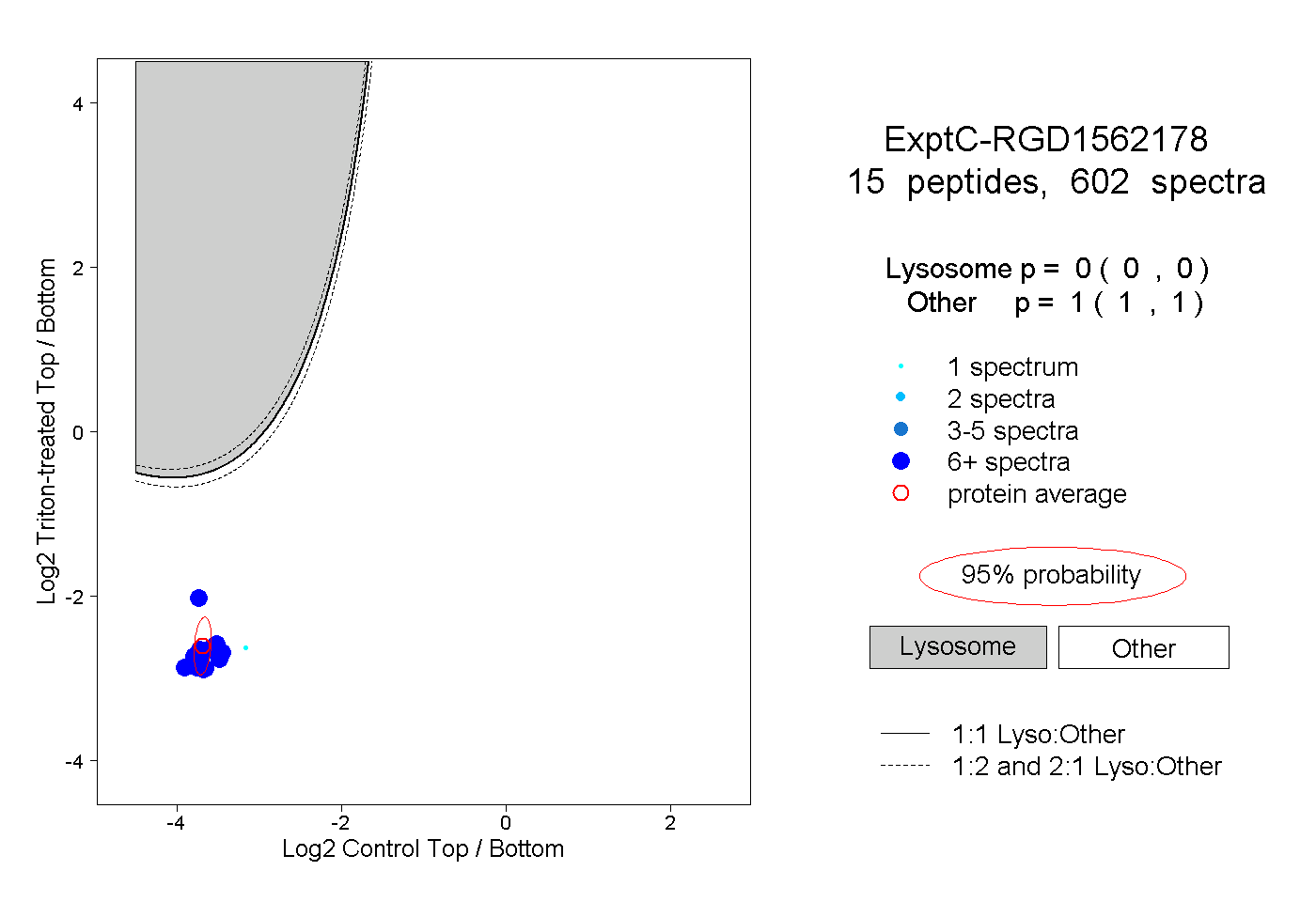 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
32 spectra |
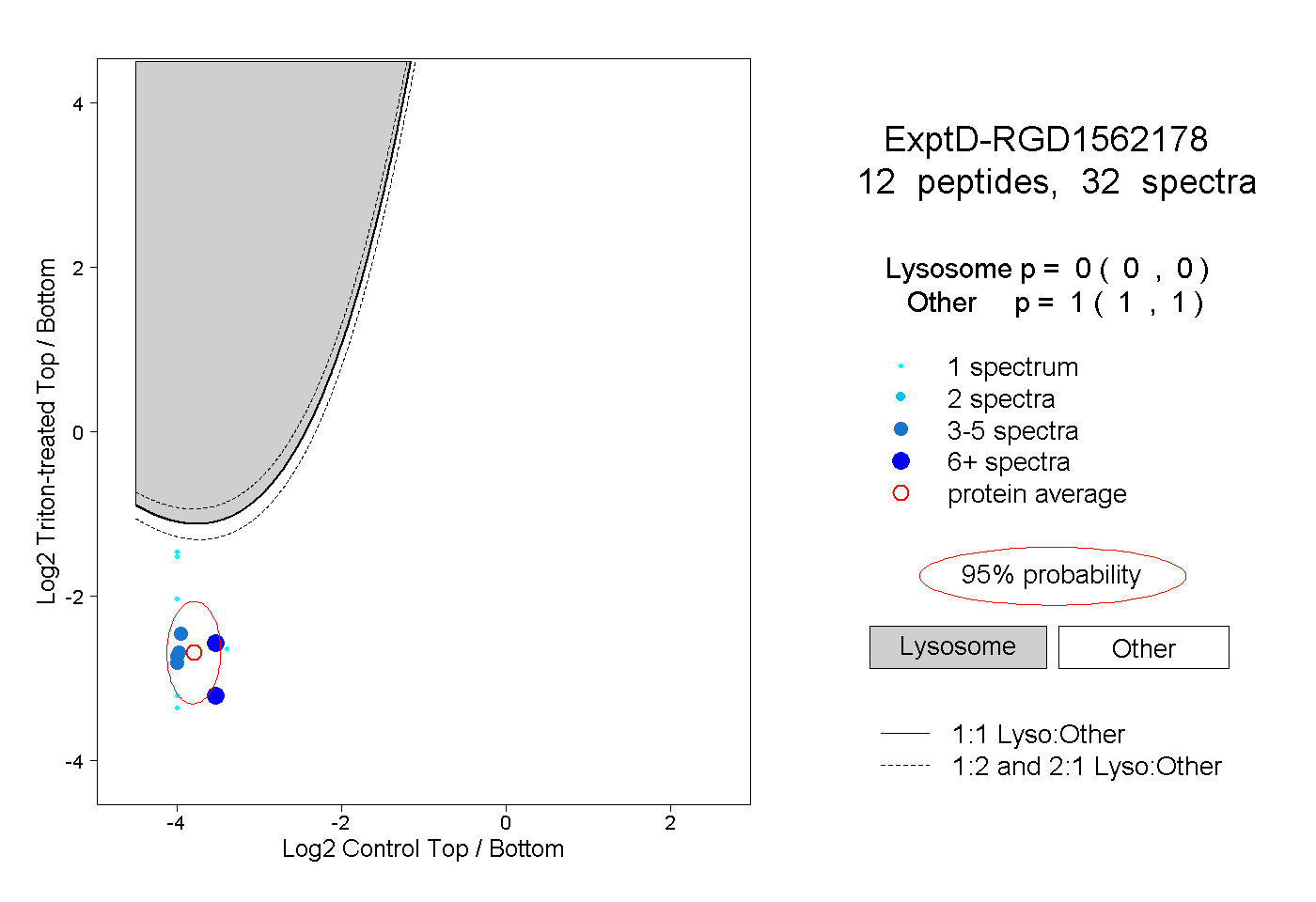 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |