peptides
spectra
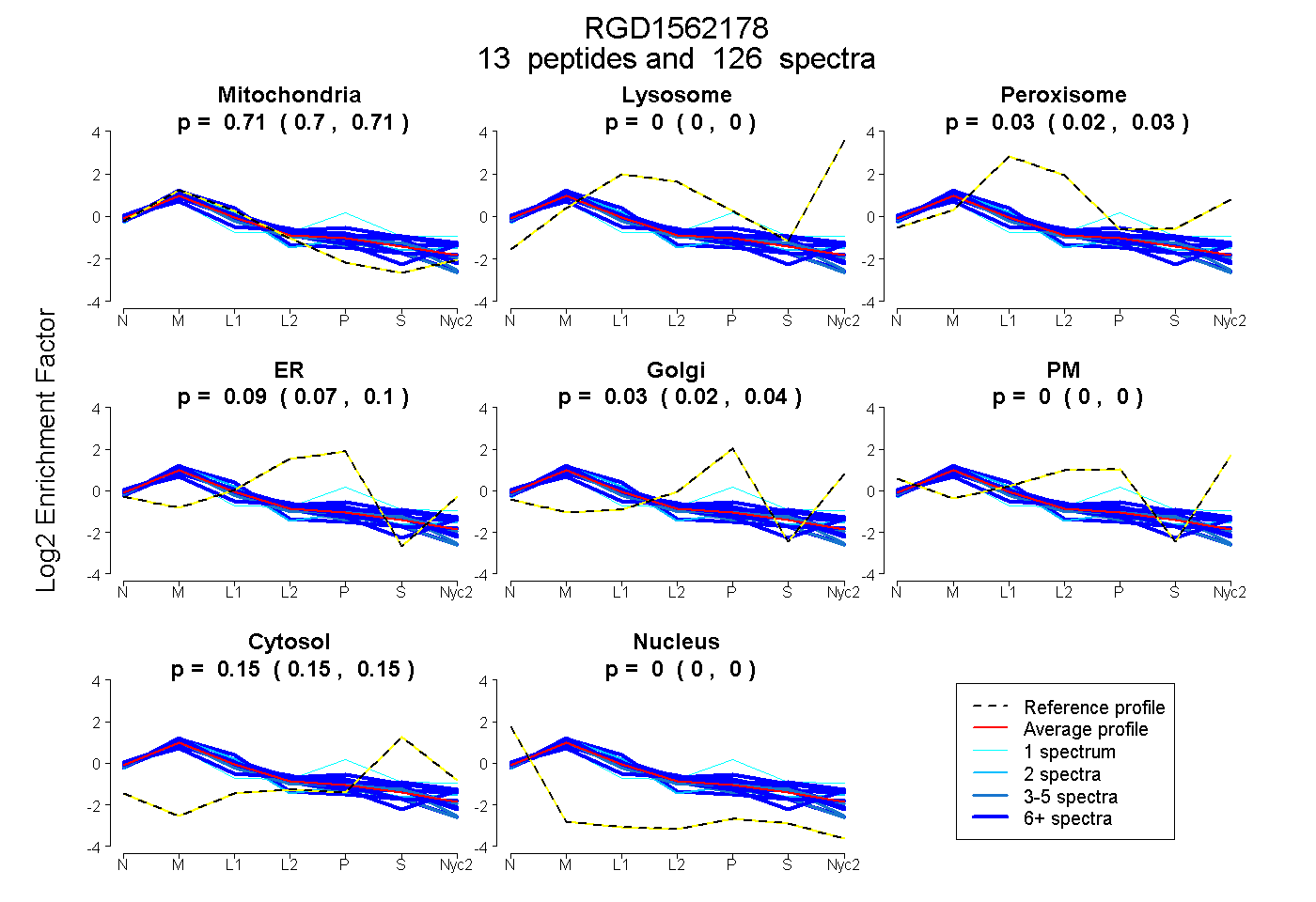
0.705 | 0.711
0.000 | 0.000
0.021 | 0.030
0.073 | 0.096
0.019 | 0.041
0.000 | 0.000
0.146 | 0.152
0.000 | 0.000
| Plot | Mito | Lyso | Perox | ER | Golgi | PM | Cytosol | Nucleus | |||||
| Expt A |
peptides |
126 spectra |
 |
0.708 0.705 | 0.711 |
0.000 0.000 | 0.000 |
0.026 0.021 | 0.030 |
0.086 0.073 | 0.096 |
0.031 0.019 | 0.041 |
0.000 0.000 | 0.000 |
0.149 0.146 | 0.152 |
0.000 0.000 | 0.000 |
| 8 spectra, AVLLGPPGAGK | 0.682 | 0.000 | 0.013 | 0.105 | 0.000 | 0.000 | 0.200 | 0.000 | ||
| 5 spectra, NLETPSCK | 0.718 | 0.000 | 0.000 | 0.073 | 0.026 | 0.000 | 0.183 | 0.000 | ||
| 1 spectrum, LAENFCVCHLATGDMLR | 0.428 | 0.000 | 0.015 | 0.000 | 0.375 | 0.000 | 0.183 | 0.000 | ||
| 3 spectra, GTQAPK | 0.786 | 0.000 | 0.008 | 0.028 | 0.000 | 0.000 | 0.178 | 0.000 | ||
| 39 spectra, QAEMLDDLMDK | 0.742 | 0.000 | 0.026 | 0.099 | 0.039 | 0.000 | 0.095 | 0.000 | ||
| 17 spectra, LVSDEMVVELIEK | 0.757 | 0.000 | 0.018 | 0.058 | 0.000 | 0.000 | 0.166 | 0.000 | ||
| 6 spectra, NGFLLDGFPR | 0.779 | 0.018 | 0.000 | 0.000 | 0.115 | 0.076 | 0.012 | 0.000 | ||
| 2 spectra, ATMDAGK | 0.758 | 0.025 | 0.008 | 0.000 | 0.105 | 0.000 | 0.104 | 0.000 | ||
| 8 spectra, AMVASGSELGK | 0.900 | 0.000 | 0.000 | 0.000 | 0.000 | 0.000 | 0.100 | 0.000 | ||
| 11 spectra, LEAYHTQTTPLVEYYR | 0.576 | 0.000 | 0.122 | 0.000 | 0.104 | 0.000 | 0.198 | 0.000 | ||
| 9 spectra, SYHEEFNPPK | 0.536 | 0.000 | 0.032 | 0.058 | 0.169 | 0.000 | 0.205 | 0.000 | ||
| 4 spectra, DDITGEPLIR | 0.808 | 0.000 | 0.000 | 0.078 | 0.000 | 0.000 | 0.096 | 0.018 | ||
| 13 spectra, APNALAPEPEHPK | 0.616 | 0.000 | 0.117 | 0.003 | 0.154 | 0.000 | 0.110 | 0.000 |
| Plot | Mito | Lyso or Perox | ER | Golgi | PM | Cytosol | Nucleus | ||||||
| Expt B |
peptides |
72 spectra |
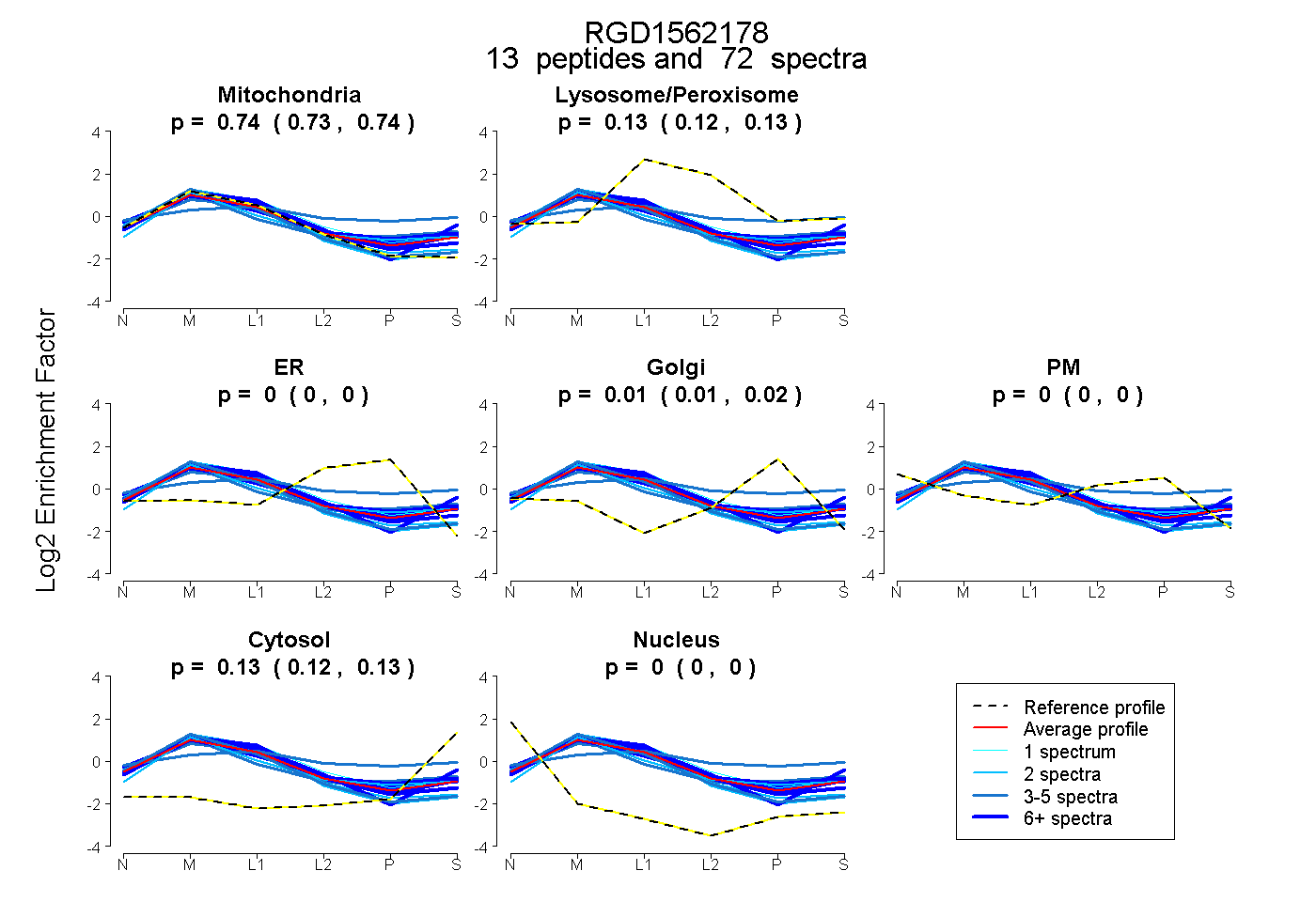 |
0.735 0.727 | 0.742 |
0.125 0.121 | 0.129 |
0.000 0.000 | 0.000 |
0.013 0.006 | 0.020 |
0.000 0.000 | 0.000 |
0.126 0.121 | 0.131 |
0.000 0.000 | 0.000 |
|||
| Plot | Lyso | Other | |||||||||||
| Expt C |
peptides |
602 spectra |
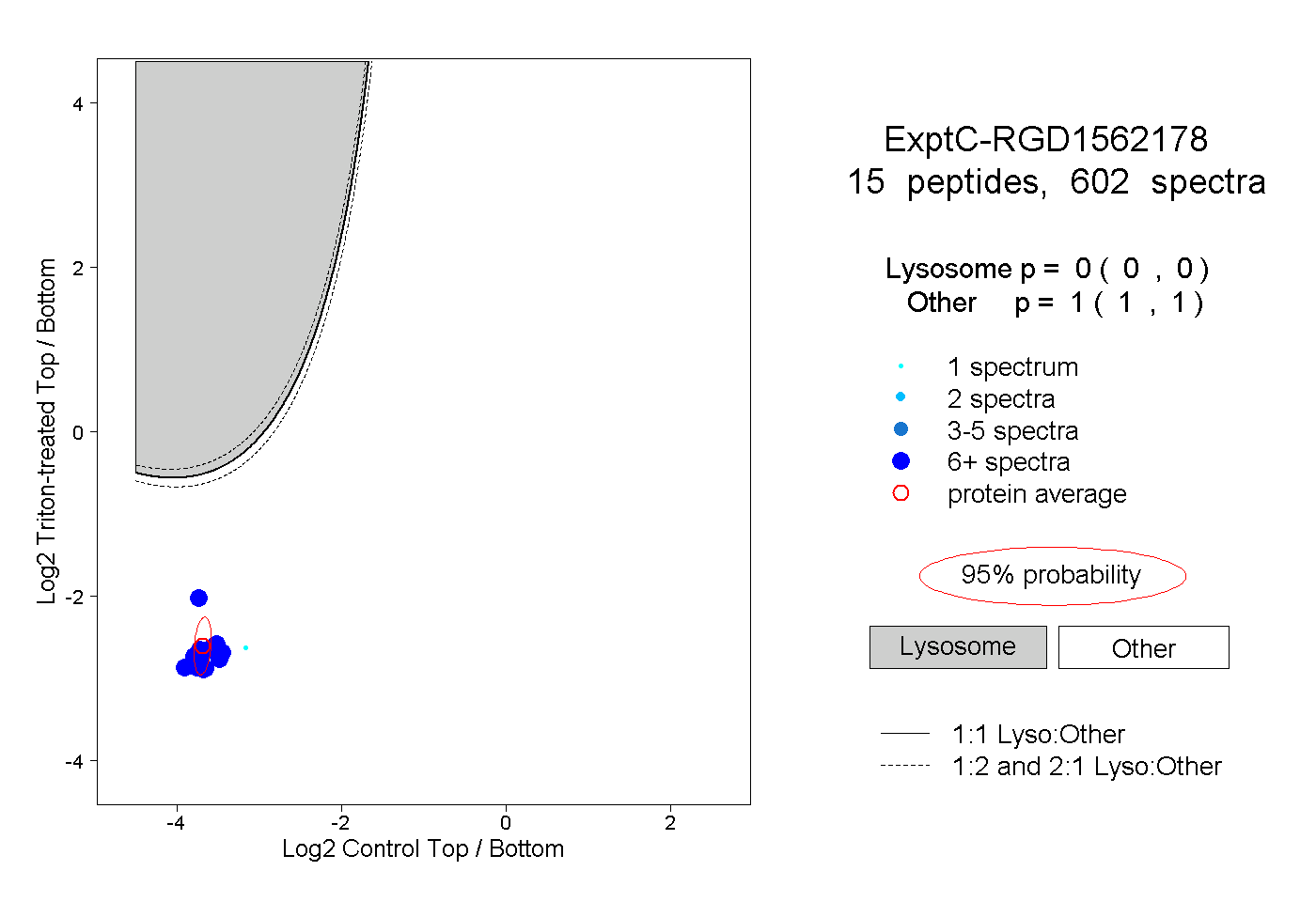 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |
||||||||
| Plot | Lyso | Other | |||||||||||
| Expt D |
peptides |
32 spectra |
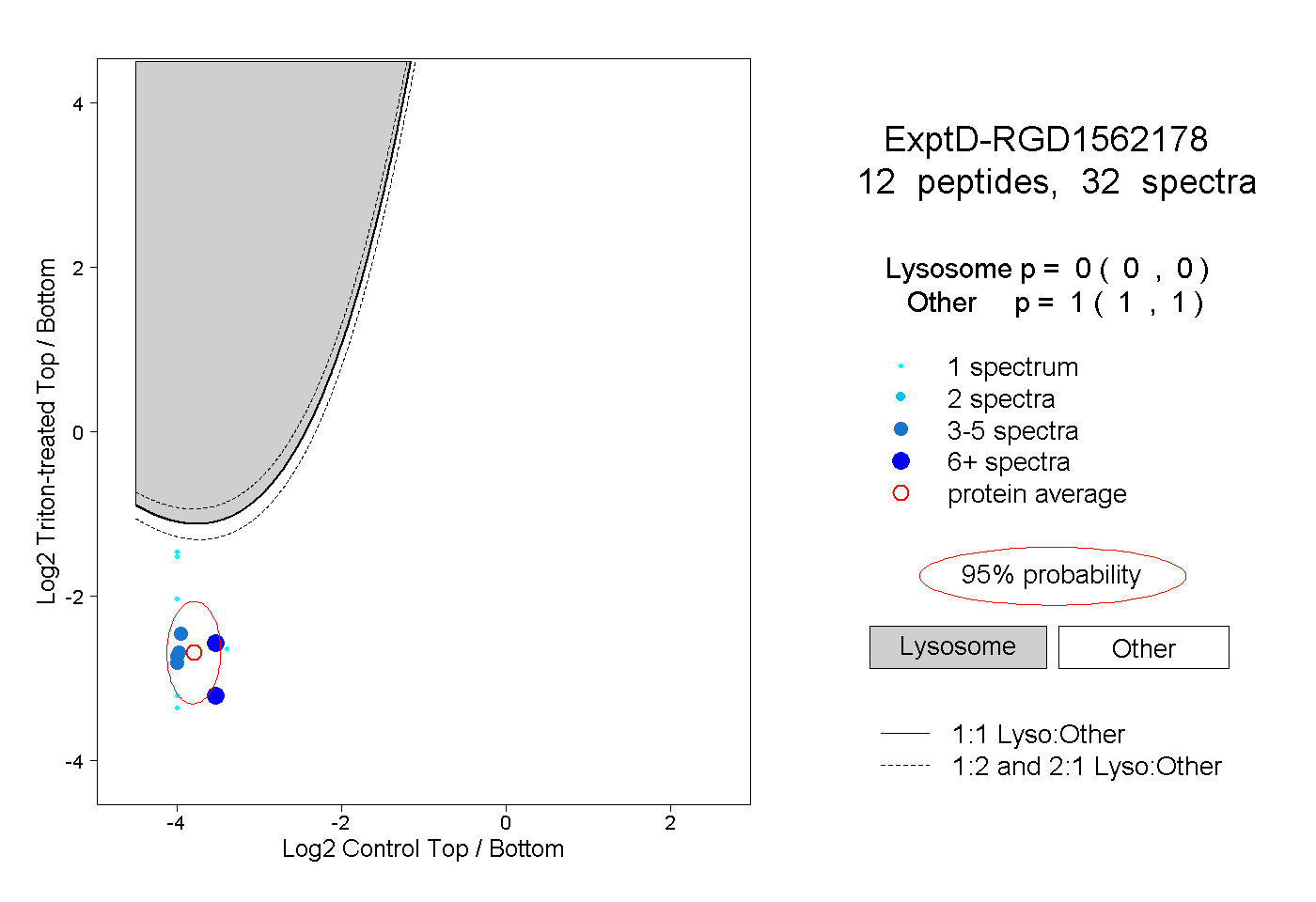 |
0.000 0.000 | 0.000 |
1.000 1.000 | 1.000 |